01/02/2006
I den medicinske og videnskabelige verden står vi ofte over for udfordringen med at identificere og klassificere de milliarder af mikroorganismer, der lever i og omkring os. Mange af disse mikrober kan ikke dyrkes i et laboratorium med traditionelle metoder, hvilket gør dem til et mysterium. For at løse dette problem har forskere udviklet kraftfulde værktøjer baseret på genetik. Et af de mest grundlæggende og vigtige koncepter i denne nye æra af mikrobiologi er den Operationelle Taxonomiske Enhed, eller OTU. Dette er ikke blot et teknisk begreb for specialister; det er en nøgle til at forstå alt fra vores tarmsundhed til udviklingen af nye behandlinger mod sygdomme.
Den grundlæggende definition: Hvad er en OTU?
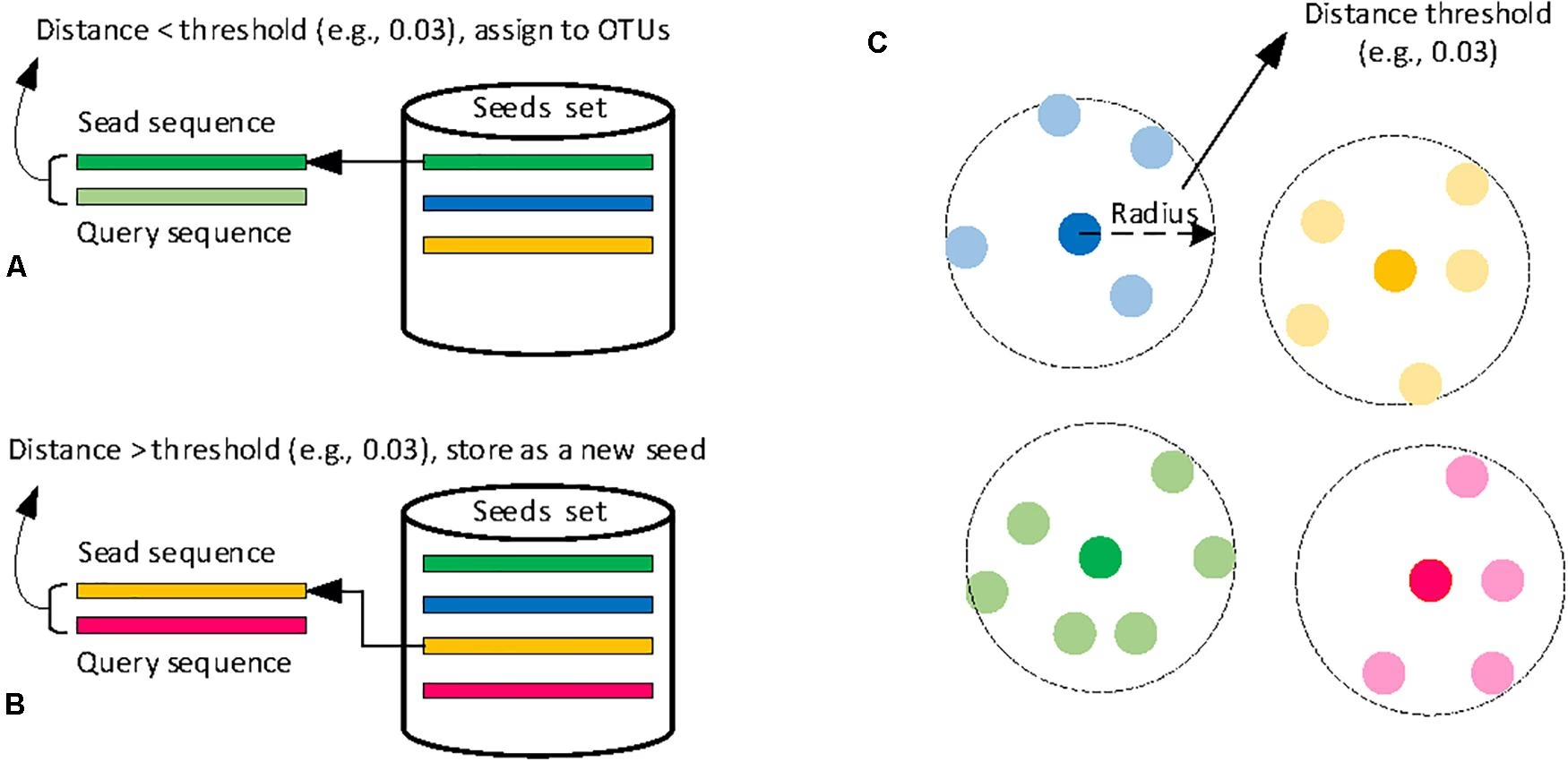
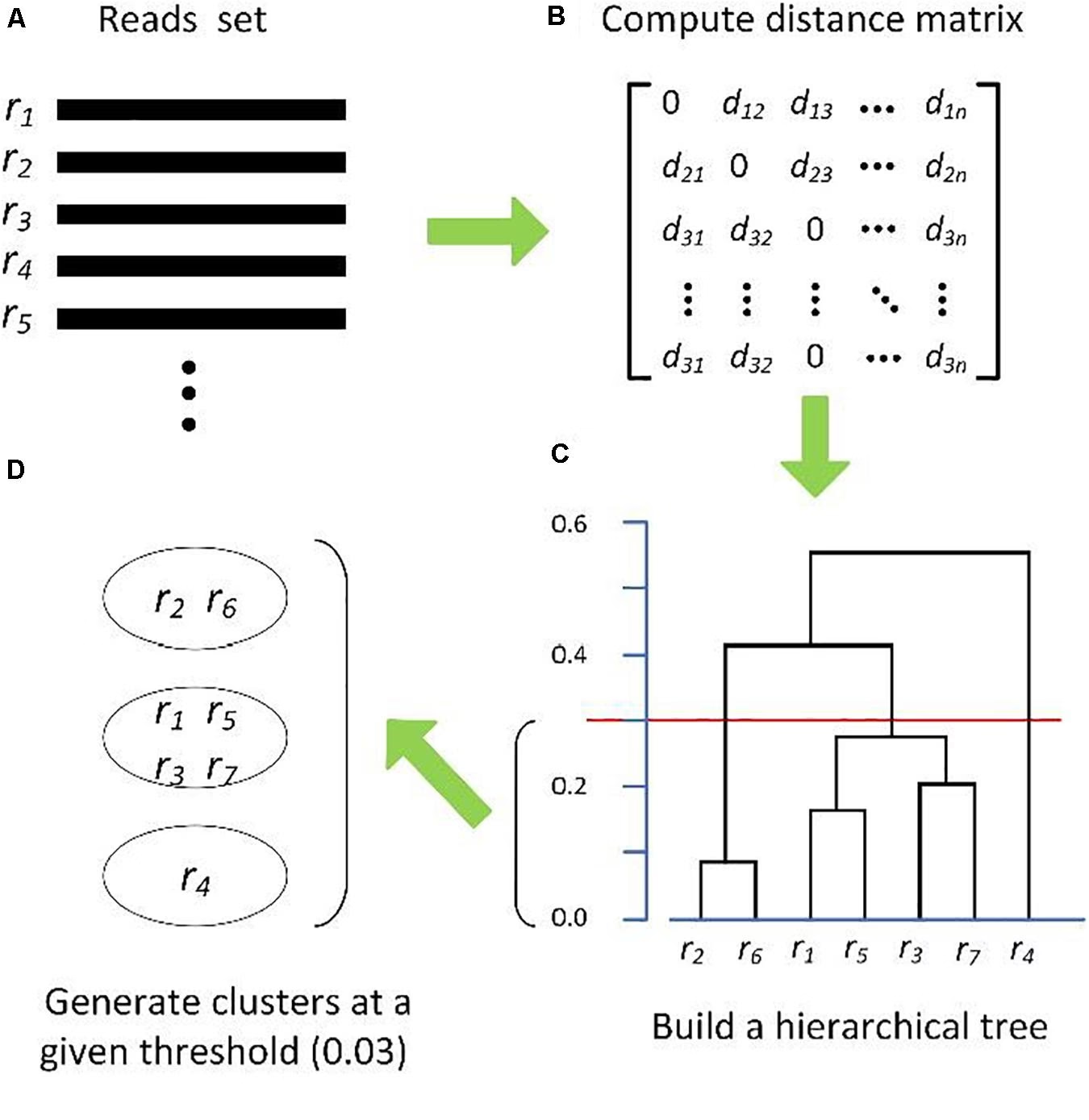
En Operationel Taxonomisk Enhed (OTU) er en pragmatisk definition, der bruges til at gruppere nært beslægtede organismer. Begrebet blev oprindeligt introduceret i 1960'erne inden for numerisk taksonomi, hvor det refererede til enhver gruppe af organismer, der blev undersøgt. I dag har begrebet dog fået en langt mere specifik og udbredt betydning, især inden for mikrobiel økologi og sundhedsvidenskab. I denne moderne kontekst refererer en OTU til en klynge af mikroorganismer, der er grupperet baseret på ligheden i deres DNA-sekvenser for et specifikt markørgen. Man kan tænke på det som en måde at skabe 'arter' på for organismer, vi ikke kan se eller klassificere på traditionel vis.
Den mest almindelige metode involverer sekventering af 16S rRNA-genet for prokaryoter (bakterier og arkæer) eller 18S rRNA-genet for eukaryoter. Disse gener er ideelle, fordi de er til stede i næsten alle organismer inden for deres domæner og har regioner, der ændrer sig langsomt over evolutionær tid, hvilket gør dem perfekte til at sammenligne slægtskab. Når forskere har sekvenserne, grupperer de dem. Den mest almindelige grænse for at definere en OTU er 97% lighed. Det betyder, at alle DNA-sekvenser, der er 97% eller mere identiske med hinanden, bliver samlet i den samme OTU. Denne tærskel er en praktisk tilnærmelse til, hvad der kunne svare til en mikrobiel art, selvom denne definition er genstand for videnskabelig debat.
Hvordan OTU'er anvendes i sundhedsforskning
Anvendelsen af OTU'er har revolutioneret vores evne til at studere komplekse mikrobielle samfund, såsom det menneskelige mikrobiom. Før disse metoder var vi begrænset til kun at studere de mikrober, der kunne dyrkes i petriskåle, hvilket menes at være mindre end 1% af alle mikrober. Nu kan vi tage en prøve fra tarmen, huden eller munden, sekventere alt DNA'et og bruge OTU-analyse til at få et fuldstændigt billede af, hvem der bor der.
Dette har enorme implikationer for medicin:
- Sygdomsdiagnostik: Forskere kan sammenligne OTU-profilerne fra sunde individer med dem fra personer med sygdomme som Crohns sygdom, irritabel tyktarm (IBS), fedme eller endda visse former for kræft. Ofte finder de signifikante forskelle i tilstedeværelsen eller fraværet af specifikke OTU'er, hvilket kan pege på nye diagnostiske markører eller årsagssammenhænge.
- Behandlingsudvikling: Ved at forstå, hvilke mikrobielle samfund der er forbundet med sundhed, kan man udvikle probiotika eller fæcestransplantationer (FMT) mere målrettet. Man kan sigte mod at genoprette manglende OTU'er eller reducere skadelige.
- Personlig medicin: Hver persons mikrobiom er unikt. I fremtiden kan analyse af en persons OTU-profil hjælpe med at skræddersy kostanbefalinger eller medicinske behandlinger for at opnå det bedste resultat baseret på deres specifikke mikrobielle sammensætning.
- Identifikation af patogener: I tilfælde af infektioner kan sekventering og OTU-analyse hurtigt identificere den sygdomsfremkaldende organisme, selvom den er sjælden eller svær at dyrke, hvilket muliggør hurtigere og mere præcis behandling.
Stabilitet og udfordringer ved OTU-metoden
Selvom OTU-analyse er et utroligt kraftfuldt værktøj, er det ikke uden udfordringer. En af de største bekymringer er stabiliteten og reproducerbarheden. Valget af bioinformatiske algoritmer og lighedstærskel (f.eks. 97% vs. 99%) kan påvirke det endelige antal og sammensætningen af OTU'er. Desuden kan fejl, der opstår under DNA-sekventeringsprocessen, fejlagtigt skabe nye, kunstige OTU'er, hvilket kan overdrive diversiteten i en prøve.
På trods af disse udfordringer har flere studier vist, at OTU'er generelt er økologisk konsistente på tværs af forskellige levesteder og analysemetoder. Det betyder, at selvom det præcise antal OTU'er kan variere lidt, vil de overordnede mønstre – for eksempel hvilke grupper der dominerer i en sund tarm versus en syg tarm – forblive de samme. Dette giver forskerne tillid til de biologiske konklusioner, de drager. For at imødegå nogle af disse problemer er nyere metoder som Amplicon Sequence Variants (ASVs) blevet populære. ASVs sigter mod at definere enheder baseret på 100% sekvenslighed, hvilket kan rette op på nogle af de fejl, der er forbundet med klyngedannelse, men OTU-konceptet er stadig udbredt og fundamentalt for meget af den eksisterende forskning.

Sammenligning: Traditionel Taksonomi vs. OTU-baseret Klassificering
For at forstå betydningen af OTU'er er det nyttigt at sammenligne dem med den klassiske Linné-taksonomi, som vi kender fra biologitimerne.
| Kriterium | Traditionel Taksonomi | OTU-baseret Klassificering |
|---|---|---|
| Basis for klassificering | Morfologi (udseende), fysiologi, adfærd | DNA-sekvenslighed af markørgener |
| Grundlæggende enhed | Art, slægt, familie | Operationel Taxonomisk Enhed (OTU) |
| Primær anvendelse | Makroskopiske organismer (dyr, planter) | Mikroorganismer (især ukultiverbare) |
| Metode | Observation, dissektion, dyrkning | Højkapacitets-sekventering, bioinformatik |
Fra data til indsigt: Visualisering af OTU'er
Når forskere har identificeret OTU'erne i deres prøver, er næste skridt at analysere og visualisere dataene. En af de mest almindelige måder at gøre dette på er ved hjælp af såkaldte 'taxa summaries'. Disse er typisk søjlediagrammer, der viser den relative overflod af forskellige OTU'er (eller de taksonomiske grupper, de tilhører, som slægter eller familier) i hver prøve. Denne type visualisering gør det meget nemt at se mønstre. Man kan hurtigt identificere, om en bestemt prøve er en outlier – altså markant anderledes end de andre. Man kan også visuelt sammenligne grupper af prøver, for eksempel en kontrolgruppe versus en behandlingsgruppe, for at se, hvilke mikrobielle grupper der ændrer sig som reaktion på en intervention. Disse visualiseringer er afgørende for at omsætte komplekse datasæt til meningsfuld biologisk og medicinsk indsigt.
Ofte Stillede Spørgsmål (FAQ)
Spørgsmål: Er en OTU det samme som en art?
Svar: Ikke præcist. En OTU er en operationel proxy for en art. Mens artsbegrebet i biologi ofte er baseret på evnen til at formere sig, er dette ikke anvendeligt for de fleste mikrober. OTU'en er i stedet baseret på en vilkårligt fastsat genetisk lighedstærskel (typisk 97%). Det er en praktisk måde at gruppere lignende organismer på, men det afspejler ikke nødvendigvis en 'biologisk art' i traditionel forstand.
Spørgsmål: Hvorfor bruger man netop 97% lighed?
Svar: Tærsklen på 97% for 16S rRNA-genet er en historisk konvention, der stammer fra tidlige studier i 1990'erne. Man observerede, at bakterier, der blev betragtet som forskellige arter baseret på ældre metoder, typisk havde mere end 3% forskel i deres 16S-sekvens. Selvom denne grænse er omdiskuteret og ikke passer perfekt på alle mikrobielle grupper, er den blevet en de facto standard, der gør det muligt at sammenligne resultater på tværs af mange forskellige studier.
Spørgsmål: Hvilken rolle spiller OTU'er for fremtidens sundhed?
Svar: OTU'er og lignende metoder er fundamentale for fremtidens personlige medicin. Ved at kunne kortlægge en persons unikke mikrobielle fingeraftryk kan læger i fremtiden skræddersy behandlinger, kost og livsstilsråd. For eksempel kan viden om en persons tarm-OTU'er hjælpe med at forudsige, hvordan de vil reagere på en bestemt type medicin eller diæt. Dette åbner op for en mere proaktiv og individualiseret tilgang til sundhed og sygdomsforebyggelse.
Hvis du vil læse andre artikler, der ligner Hvad er en Operationel Taxonomisk Enhed (OTU)?, kan du besøge kategorien Sundhed.