14/08/2001
I en tid hvor medicinske fremskridt sker med lynets hast, er begrebet personlig medicin ikke længere science fiction, men en hastigt voksende virkelighed. Forestil dig en behandling, der ikke er designet til den 'gennemsnitlige' patient, men er skræddersyet præcist til din unikke genetiske profil. Dette er kernen i personlig medicin, og et af de mest afgørende værktøjer, der driver denne revolution, er Drug-Gene Interaction Database, bedre kendt som DGIdb. Denne database fungerer som et digitalt leksikon, der hjælper forskere og læger med at navigere i det komplekse landskab af menneskelige gener og deres interaktioner med lægemidler. Den bygger bro mellem genetisk forskning og klinisk praksis, og åbner døren for mere effektive og målrettede behandlinger.
Hvad er DGIdb helt præcist?
Drug-Gene Interaction Database (DGIdb) er en open-source, offentligt tilgængelig database, der samler og organiserer information om, hvordan lægemidler og gener påvirker hinanden. Den blev udviklet for at imødekomme en kritisk udfordring i moderne medicin: Når forskere identificerer en liste over gener, der er muteret eller ændret i en patients sygdom (f.eks. en kræftsvulst), hvordan finder de så ud af, om der findes lægemidler, der kan målrette disse specifikke gener? Før DGIdb var denne proces en utrolig tidskrævende og manuel opgave, der krævede gennemgang af utallige videnskabelige artikler, kliniske forsøgsdata og andre databaser.
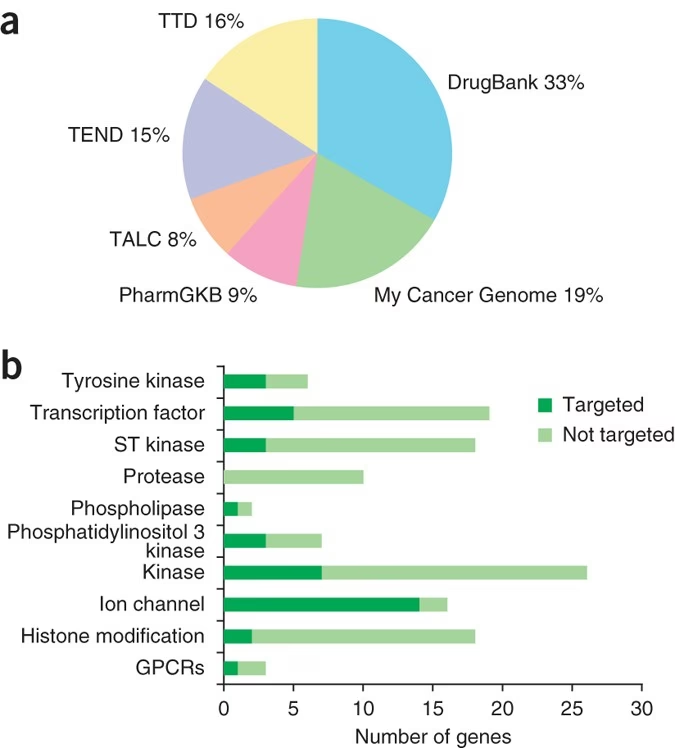
DGIdb automatiserer og forenkler denne proces. Ved at kombinere data fra en lang række anerkendte kilder som DrugBank, PharmGKB og ClinicalTrials.gov, skaber den et samlet, søgbart system. Den indeholder information om titusindvis af gener og tusindvis af lægemidler, der er involveret i over 15.000 kendte lægemiddel-gen-interaktioner. Med et par klik kan en forsker eller kliniker indtaste en liste af gener og modtage en omfattende rapport over alle kendte eller potentielle lægemiddelinteraktioner relateret til disse gener.
To Søjler i Databasen: Kendte Interaktioner og Potentielle Mål
For at organisere denne enorme mængde data, arbejder DGIdb med to hovedkategorier, som tilsammen udgør det, forskere kalder det "druggable genome" – den del af vores genom, som potentielt kan påvirkes af lægemidler.
Den første kategori omfatter kendte lægemiddel-gen interaktioner. Dette er veletablerede forbindelser, hvor man ved, at et specifikt lægemiddel interagerer med et specifikt gen eller det protein, genet koder for. Disse oplysninger er uvurderlige, når en læge står med en patient, hvis sygdom er drevet af en kendt genmutation. Ved at slå genet op i DGIdb kan lægen hurtigt se, om der allerede findes godkendte lægemidler, der kan hæmme eller på anden måde modulere dette gens aktivitet. Dette er grundlaget for mange målrettede behandlinger, især inden for kræft.
Den anden kategori dækker over potentielt 'druggable' gener. Dette er gener, der måske ikke i øjeblikket har et kendt lægemiddel rettet mod sig, men som tilhører genfamilier eller har molekylære funktioner, der gør dem til lovende mål for fremtidig lægemiddeludvikling. Eksempler på dette er kinaser og ionkanaler, som er proteintyper, der historisk set har vist sig at være gode mål for små molekyle-lægemidler. Ved at identificere disse gener kan forskere prioritere deres indsats og fokusere på at udvikle nye terapier mod hidtil ubehandlede genetiske årsager til sygdom.
Hvem bruger DGIdb og hvorfor er det så vigtigt?
DGIdb er et essentielt værktøj, der bygger bro mellem to verdener: den grundlæggende genomforskning og den kliniske patientbehandling.
For forskere, især inden for kræftforskning, er databasen en guldgrube. Når de analyserer data fra store genom-projekter og identificerer hundredvis af potentielle 'driver'-gener i kræft, hjælper DGIdb dem med at sortere og prioritere. Hvilke af disse gener er allerede kendte mål for lægemidler? Hvilke tilhører 'druggable' genfamilier og bør undersøges nærmere for ny lægemiddeludvikling? Databasen fungerer som et filter, der hjælper med at omdanne rå data til meningsfulde hypoteser.
For læger og klinikere er DGIdb et skridt på vejen mod at realisere potentialet i personlig medicin. Når en patient får foretaget en genetisk analyse af deres tumor, kan resultatet være en lang liste af mutationer. DGIdb hjælper med at oversætte denne liste til potentielle behandlingsmuligheder. Selvom databasen ikke giver endelige svar, kan den fremhæve muligheder for målrettet terapi, som måske ellers ville blive overset, og dermed understøtte lægens beslutningsproces i samråd med patienten.
Sammenligning: Traditionel vs. Personlig Medicin
For at illustrere betydningen af værktøjer som DGIdb, kan vi sammenligne den traditionelle tilgang til behandling med den personlige, datadrevne tilgang.
| Parameter | Traditionel Behandling | Personlig Medicin (med DGIdb) |
|---|---|---|
| Tilgang | "One-size-fits-all". Behandling baseret på sygdomstype (f.eks. lungekræft). | Skræddersyet. Behandling baseret på patientens specifikke genetiske profil. |
| Mål | Brede mekanismer, f.eks. at dræbe alle hurtigt delende celler (kemoterapi). | Specifikke molekylære mål (muterede gener/proteiner), der driver sygdommen. |
| Effektivitet | Variabel. Virker godt for nogle, men slet ikke for andre. | Potentielt meget højere for patienter med det rette genetiske match. |
| Bivirkninger | Ofte betydelige, da behandlingen også rammer raske celler. | Generelt færre og mere specifikke, da behandlingen er mere målrettet. |
Begrænsninger og Fremtidsperspektiver
Det er vigtigt at understrege, at DGIdb er et værktøj til hypotesegenerering, ikke en facitliste. Databasen garanterer ikke, at en given lægemiddel-gen-interaktion vil være en effektiv behandling for en specifik patient. Den tager ikke højde for den specifikke type mutation i et gen, og den erstatter på ingen måde en læges kliniske vurdering. Alle de oplysninger, der hentes fra DGIdb, skal fortolkes af eksperter – onkologer, genetikere og farmaceuter – som kan sætte dem ind i en større klinisk kontekst.
Trods disse begrænsninger er DGIdb et monumentalt skridt fremad. Den repræsenterer en kraftfuld ressource, der demokratiserer adgangen til kompleks genomisk viden. I takt med at vores forståelse af genetik og sygdomme vokser, vil databaser som DGIdb blive endnu mere centrale. De er motoren i en ny æra af kræftbehandling og medicin generelt, hvor behandlinger bliver smartere, mere præcise og i sidste ende mere effektive for den enkelte patient.
Ofte Stillede Spørgsmål (FAQ)
- Kan jeg som patient selv bruge DGIdb til at finde en behandling?
- Nej, DGIdb er et komplekst forskningsværktøj designet til fagfolk med en dybdegående forståelse af genetik og farmakologi. Oplysningerne kræver ekspertfortolkning for at være meningsfulde og sikre. Tal altid med din læge om dine behandlingsmuligheder.
- Er DGIdb kun relevant for kræft?
- Selvom databasen har et stærkt fokus på kræft, hvor genetiske analyser er mest udbredte, er principperne og dataene relevante for en bred vifte af andre sygdomme med en genetisk komponent, herunder arvelige sygdomme og visse hjertesygdomme.
- Hvad betyder "druggable genome"?
- Det "druggable genome" refererer til den delmængde af alle menneskelige gener, som koder for proteiner, der potentielt kan påvirkes af et lægemiddel. Det er i bund og grund en liste over alle de potentielle 'mål' i kroppen, som medicinalindustrien kan sigte efter, når de udvikler nye lægemidler.
- Hvem står bag DGIdb?
- DGIdb blev udviklet af forskere ved The Genome Institute ved Washington University School of Medicine. Det er et akademisk projekt, der stilles gratis til rådighed for det globale forskningssamfund for at fremme videnskabelige opdagelser og forbedre patientbehandlingen.
Hvis du vil læse andre artikler, der ligner DGIdb: Databasen der former fremtidens medicin, kan du besøge kategorien Sundhed.
